TP 3
Multilevel Analyse von Magenkarzinomdaten
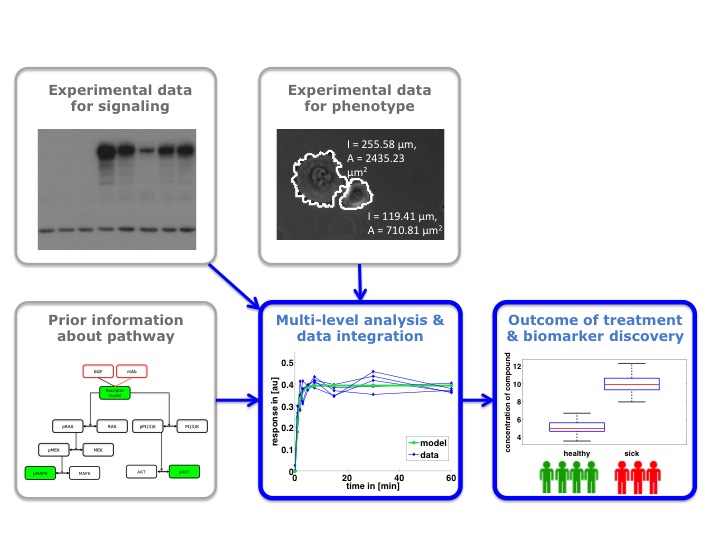
Das Ziel dieses Konsortiums ist es den Zusammenhang von molekularen Mechanismen und dem Behandlungserfolg HER2 und EGFR basierter Therapien für Magenkarzinome besser zu verstehen. Auf diese Weise wollen wir Biomarker für die Stratifizierung von Patienten identifizieren und später validieren. Die Daten für die Untersuchung werden in den Teilprojekten 1, 4 und 5 dieses Konsortiums experimentell erhoben bzw. von Teilprojekten 2 aus vorhandener Literatur extrahiert und in Teilprojekten 3 statistisch analysiert. Hierfür werden sowohl klassische statistische Verfahren verwendet als auch ein neues zweistufige Analyseverfahren, das im Rahmen dieses Projektes entwickelt wird. Dieses neue Verfahren korreliert in Schritt 1 molekulare Eigenschaften mit zellulären Phänotypen, wie z.B. Zellbeweglichkeit und in Schritt 2 zelluläre Phänotypen mit dem Behandlungserfolg. Mit dieser Kombination von neuen, hochwertigen experimentellen Daten und maßgeschneiderten statistischen Methoden werden wir unser Verständnis von Magenkarzinomen deutlich verbessern.
Aus dem Gesamtziel von Teilprojekt 3 leiten sich drei wissenschaftliche Arbeitspakete ab.
1) Analyse der Korrelation zwischen den molekularen Eigenschaften und dem zellulären Phänotyp einzelner Zelllinien.
2) Rekonstruktion der Signalwege von Cetuximab und Trastuzumab in Magenkarzinomen, basierend auf Korrelationsinformationen und verfügbarer semantischer Information, sowie die Entwicklung von probabilistischen Modellen für die Integration in das Bewegungsmodell.
3) Validierung der rekonstruierten Signalwege und der Phänotypvorhersage unter Verwendung von MALDI Imaging Massenspektrometrie Daten. Multivariate statistische Analyse und Extraktion und Validierung von Markerprofilen.
Keywords: statistische Modelle, mechanistische Modelle, Biomarker, Netzwerkrekonstruktion



