TP 1 - PeriNAA
Datengetriebene mechanistische Modellierung des N-Acetylaspartatstoffwechsels
Die Canavan-Krankheit ist eine Leukodystrophie, die aufgrund einer Defizienz des Enzyms Aspartoacylase zur einer pathologischen Anreicherung von N-Acetylaspartat (NAA) im Gehirn führt. Damit einher gehen schwerste Entwicklungsstörungen, umfassende Behinderungen und ein kurze Lebenserwartung. Bis heute sind die genauen Krankheitsmechanismen nur wenig verstanden und die Krankheit gilt als unheilbar. Behandlungsmöglichkeiten beschränken sich deshalb weitestgehend auf palliative Therapien. Es mehren sich jedoch die Hinweise, dass der NAA Stoffwechsel auch in peripheren Organen eine wichtige Rolle einnimmt, so zum Beispiel im Fettgewebe, in Immunzellen und in Lungen- und Prostatakrebszellen. Der Zusammenhang von erhöhtem NAA in peripheren Geweben für die Krankheitsentstehung bei CD-Patienten ist jedoch völlig unklar.
Um ein mechanistisches Verständnis der Funktion des NAA-Stoffwechsels im zellulären Stoffwechsel und Signalprozessen zu erlangen, werden wir mit Hilfe gerichteter und ungerichteter Isotopen-gestützter Metabolomikmethoden, sowie RNA-Sequenzierung, den Stoffwechsel von genetisch Veränderten Zelllinien, primären Zellen, Geweben von Canavan-Mausmodellen sowie Bioproben von Canavan-Patienten untersuchen. Die erhobenen Daten sollen mittels mechanistischer Computermodelle des Stoffwechsel integriert werden.
Wir werden dynamische Computermodelle des zellulären Stoffwechsels basierend auf gewöhnlichen Differentialgleichungssystemen erstellen und anhand von Massenspektrometriedaten und Sequenzierungsdaten parametrisieren. Anhand dieser Modelle werden wir Hypothesen bezüglich der Funktion von NAA in Stoffwechsel- und Signalprozessen generieren, die von den Verbundpartnern experimentell validiert werden und so iterativ unser Verständnis dieser Prozesse verbessern sollen. Im Laufe des Projekts wollen wir auch patientenspezifische Modelle generieren um etwaige Unterschiede zwischen einzelnen Patienten zu erklären.
Das Ziel dieses Teilprojekts ist es dynamische metabolische Flussanalysemethoden weiterzuentwickeln und zur integrativen Analyse des NAA-Stoffwechsels einzusetzen. Hierzu sollen Modelle und Software für die integrative Analyse der in den anderen Teilprojekten erhobenen Daten entwickelt und angewandt werden. Es sollen iterativ Hypothesen generiert werden die vom Verbundspartnern experimentell validiert werden und helfen sollen die Implikationen des NAA Stoffwechsels zu entschlüsseln.
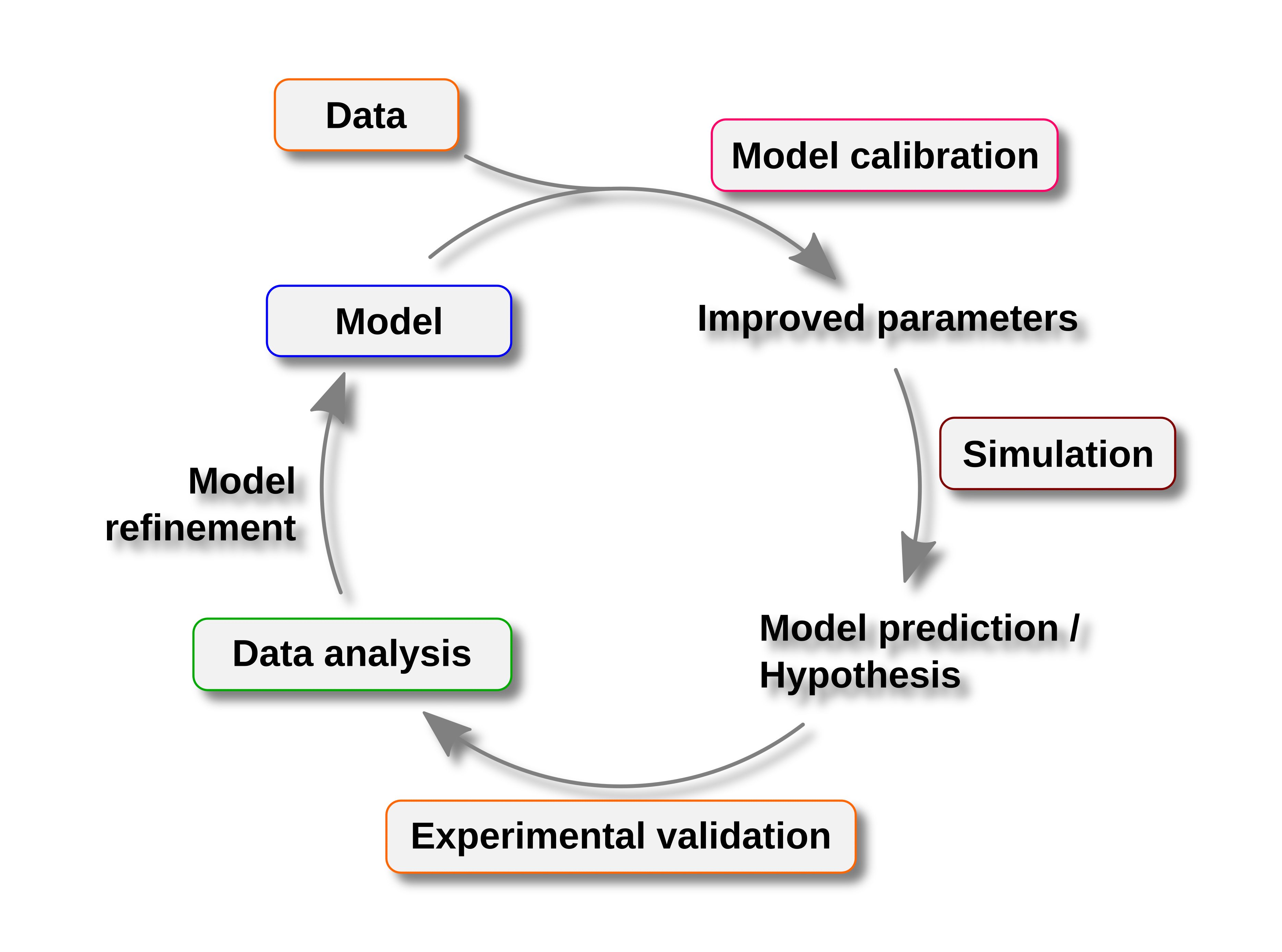
Iterative Modelverbesserung und Validierung. Ein erstes Modell wird kalibriert und es werden Modellvorhersagen gemacht. Diese Vorhersagen werden von den Partnern experimentell validiert und das Modell entsprechend angepasst, sodass wir iterativ unser Verständnis der modellierten Prozesse vertiefen können.



